如何用SVM进行乳腺癌检测
上篇文章中,详细介绍了如何创建和使用SVM分类器后,我们来看一个实际的项目,数据集来自美国威斯康星州的乳腺癌诊断数据集。
医疗人员采集了患者乳腺肿块经过细针穿刺(FNA)后的数字化图像,并且对这些数字图像进行了特征提取,这些特征可以描述图像中的细胞核呈现。肿瘤可以分成良性和恶性。部分数据截屏如下所示:
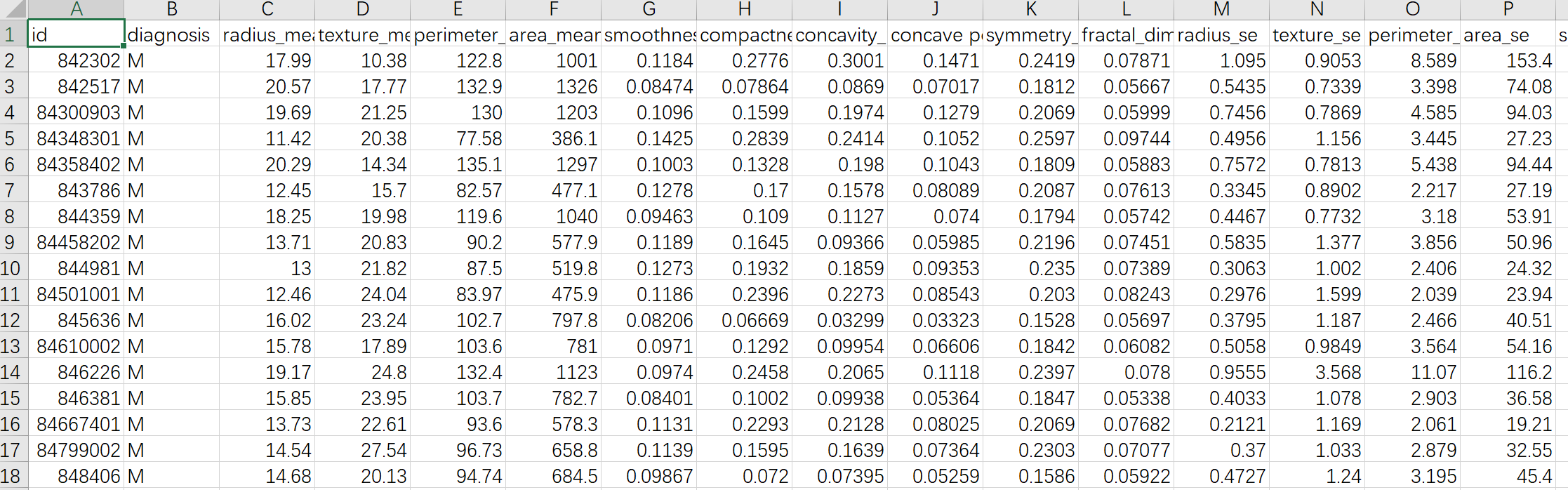
数据表一共包括了32个字段,代表的含义如下:
| 字段 | 含义 |
|---|---|
| id | ID标识 |
| diagnosis | M/B(M:恶性,B:良性) |
| radius_mean | 半径平均值 |
| texture_mean | 文理(灰度值的标准差)平均值 |
| perimeter_mean | 周长平均值 |
| area_mean | 面积平均值 |
| smoothness_mean | 平滑程度(半径内的局部变化)平均值 |
| compactness_mean | 紧密度(=周长*周长/面积-1.0)平均值 |
| concavity_mean | 凹度(轮廓凹部的严重程度)平均值 |
| concave points_mean | 凹缝(轮廓的凹部分)平均值 |
| symmetry_mean | 对称性平均值 |
| fractal_dimension_mean | 分形维数(=海岸线近似-1)平均值 |
| radius_se | 半径标准差 |
| texture_se | 文理(灰度值的标准差)标准差 |
| perimeter_se | 周长标准差 |
| area_se | 面积标准差 |
| smoothness_se | 平滑程度(半径内的局部变化)标准差 |
| compactness_se | 紧密度(=周长*周长/面积-1.0)标准差 |
| concavity_se | 凹度(轮廓凹部的严重程度)标准差 |
| concave points_se | 凹缝(轮廓的凹部分)标准差 |
| symmetry_se | 对称性标准差 |
| fractal_dimension_se | 分形维数(=海岸线近似-1)标准差 |
| radius_worst | 半径最大值 |
| texture_worst | 文理(灰度值的标准差)最大值 |
| perimeter_worst | 周长最大值 |
| area_worst | 面积最大值 |
| smoothness_worst | 平滑程度(半径内的局部变化)最大值 |
| compactness_worst | 紧密度(=周长*周长/面积-1.0)最大值 |
| concavity_worst | 凹度(轮廓凹部的严重程度)最大值 |
| concave points_worst | 凹缝(轮廓的凹部分)最大值 |
| symmetry_worst | 对称性最大值 |
| fractal_dimension_worst | 分形维数(=海岸线近似-1)最大值 |
上面的表格中,mean代表平均值,se代表标准差,worst代表最大值(3个最大值的平均值)。每张图像都计算了相应的特征,得出了这30个特征值(不包括ID字段和分类标识结果字段diagnosis),实际上是10个特征值(radius、texture、perimeter、area、smoothness、compactness、concavity、concave points、symmetry和fractal_dimension_mean)的3个维度,平均、标准差和最大值。这些特征值都保留了4位数字。字段中没有缺失的值。在569个患者中,一共有357个是良性,212个是恶性。
好了,我们的目标是生成一个乳腺癌诊断的SVM分类器,并计算这个分类器的准确率。首先设定项目的执行流程:
- 首先我们需要加载数据源;
- 在准备阶段,需要对加载的数据源进行探索,查看样本特征和特征值,这个过程你也可以使用数据可视化,它可以方便我们对数据及数据之间的关系进一步加深了解。然后按照“完全合一”的准则来评估数据的质量,如果数据质量不高就需要做数据清洗。数据清洗之后,你可以做特征选择,方便后续的模型训练;
- 在分类阶段,选择核函数进行训练,如果不知道数据是否为线性,可以考虑使用SVC(kernel=‘rbf’) ,也就是高斯核函数的SVM分类器。然后对训练好的模型用测试集进行评估。
按照上面的流程,我们来编写下代码,加载数据并对数据做部分的探索:
1 | import pandas as pd |
探索结果如下:
1 | Index(['id', 'diagnosis', 'radius_mean', 'texture_mean', 'perimeter_mean', |
下一步,是对数据进行清洗。
运行结果中,你能看到32个字段里,id是没有实际含义的,可以去掉。diagnosis字段的取值为B或者M,我们可以用0和1来替代。另外其余的30个字段,其实可以分成三组字段,下划线后面的mean、se和worst代表了每组字段不同的度量方式,分别是平均值、标准差和最大值。
1 | # 将特征字段分成3组 |
然后我们要做特征选择,首先需要观察下features_mean各变量之间的关系,这里我们可以用DataFrame的corr()函数,然后用热力图帮我们可视化呈现。同样,我们也会看整体良性、恶性肿瘤的诊断情况。
1 | # 将肿瘤诊断结果可视化 |
具体运行的结果如下:
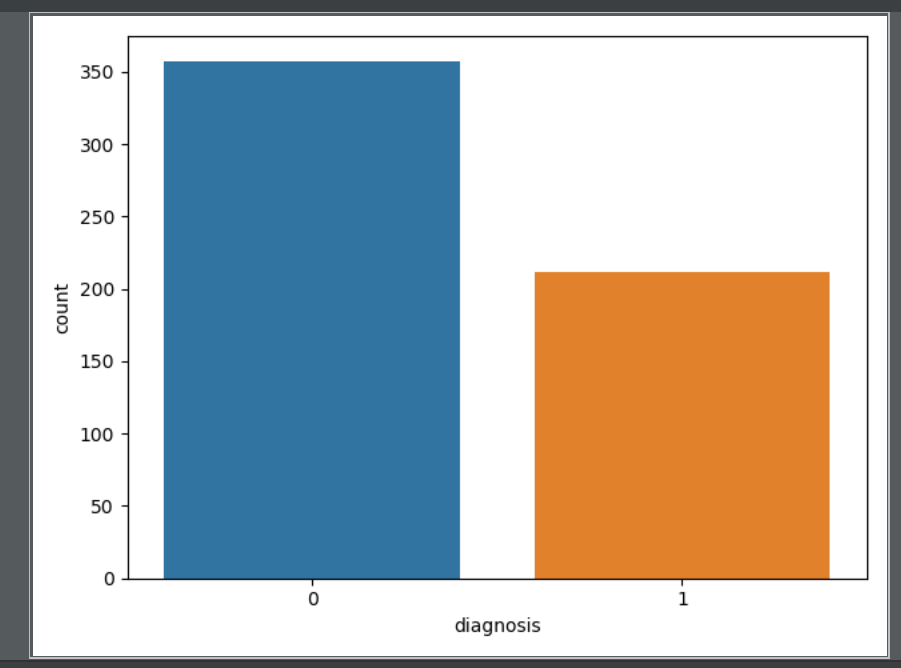
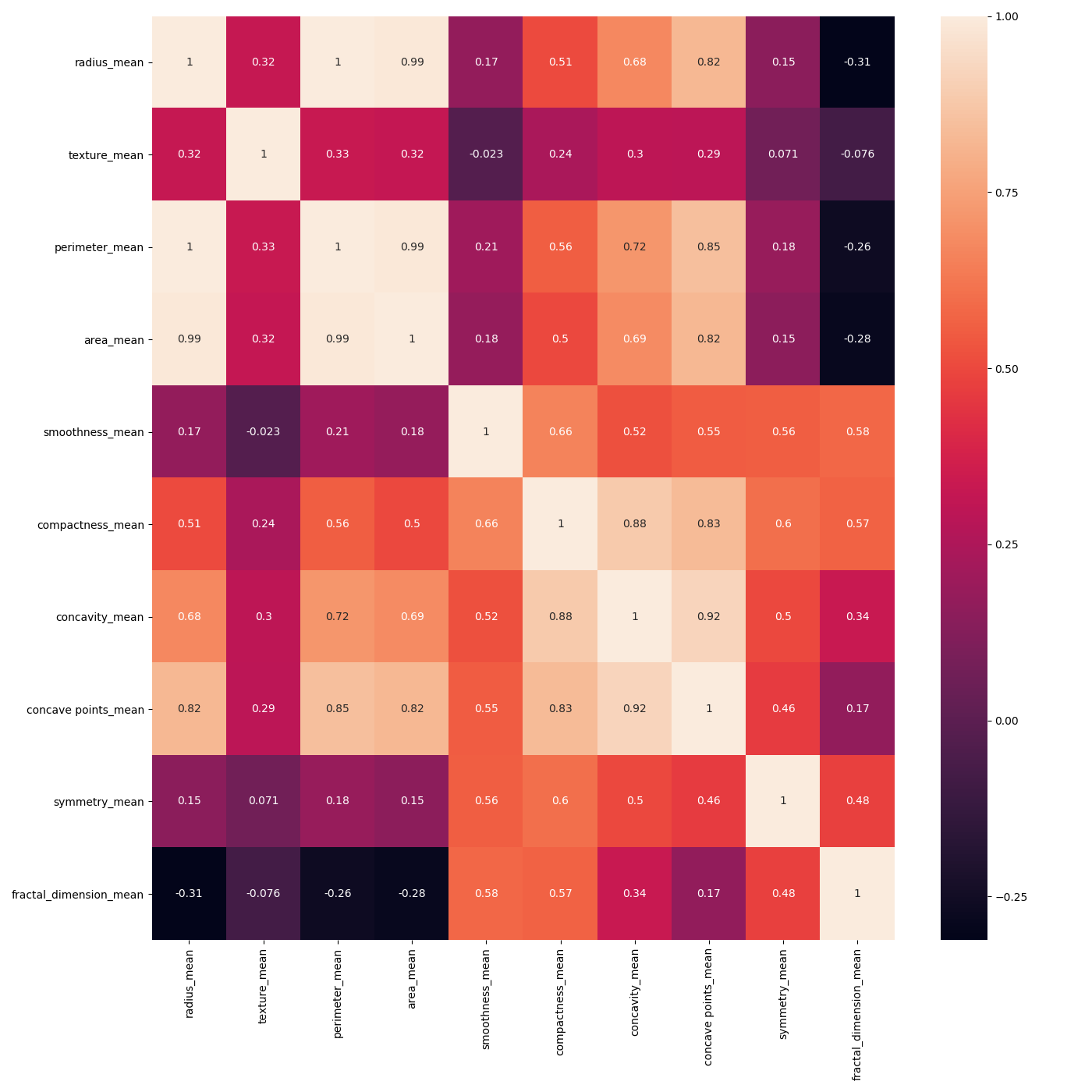
热力图中对角线上的为单变量自身的相关系数是1。颜色越浅代表相关性越大。分析热力图可以得出:radius_mean、perimeter_mean和area_mean相关性非常大,compactness_mean、concavity_mean、concave_points_mean这三个字段也是相关的,因此我们可以取其中的一个作为代表。
那么如何进行特征选择呢?
特征选择的目的是降维,用少量的特征代表数据的特性,这样也可以增强分类器的泛化能力,避免数据过拟合。
我们能看到mean、se和worst这三组特征是对同一组内容的不同度量方式,我们可以保留mean这组特征,在特征选择中忽略掉se和worst。同时我们能看到mean这组特征中,radius_mean、perimeter_mean、area_mean这三个属性相关性大,compactness_mean、daconcavity_mean、concave points_mean这三个属性相关性大。我们分别从这2类中选择1个属性作为代表,比如radius_mean和compactness_mean。
这样我们就可以把原来的10个属性缩减为6个属性,代码如下:
1 | # 特征选择 |
对特征进行选择之后,我们就可以准备训练集和测试集:
1 | # 抽取30%的数据作为测试集,其余作为训练集 |
在正式开始建模前,需要对数据进行规范化处理。采用Z-Score规范化数据,保证每个特征维度的数据均值为0,方差为1,具体代码如下:
1 | # 采用Z-Score规范化数据,保证每个特征维度的数据均值为0,方差为1 |
最后,可以用SVM模型对规范化后的数据进行训练和预测,具体如下:
1 | # 创建SVM分类器 |
得到的结果如下:
1 | 准确率: 0.9005847953216374 |
准确率大于90%,说明模型训练的结果还不错。